Dans le domaine de la biologie structurale, les avancées technologiques permettent d’explorer des territoires jusqu’alors inaccessibles. Récemment, des chercheurs d’Apple ont fait un bond significatif avec le développement de leur modèle SimpleFold, une alternative prometteuse aux méthodes existantes pour prédire la structure tridimensionnelle des protéines. Cette avancée offre de nouvelles perspectives dans la recherche et le développement de médicaments.
Comprendre les enjeux de la prédiction des structures protéiques
Jusqu’à il y a peu, estimer la structure d’une protéine à partir de sa séquence d’acides aminés représentait un défi colossal. Les méthodes traditionnelles, comme AlphaFold, nécessitaient des mois, parfois des années, de calculs intensifs.
Avec l’émergence de modèles récents tels qu’AlphaFold2, RoseTTAFold, et ESMFold, ce processus a pu être réduit à quelques heures, voire minutes. Chaque modèle utilise des techniques spécifiques, mais ceux-ci demandent des ressources computationnelles considérables.
Les chercheurs d’Apple remarquent que même si ces modèles ont atteint des niveaux d’excellence, ils se basent sur des architectures complexes, reliant diverses approches. Leurs travaux visent à simplifier ce schéma en explorant une méthode innovante.
Le modèle SimpleFold : une approche novatrice
Le modèle SimpleFold se démarque par son utilisation de modèles de correspondance de flux, introduits en 2023. Contrairement aux méthodes complexes d’alignement de séquences, SimpleFold opte pour une approche qui minimise les étapes de débruitage, rendant le processus moins coûteux en calculs.
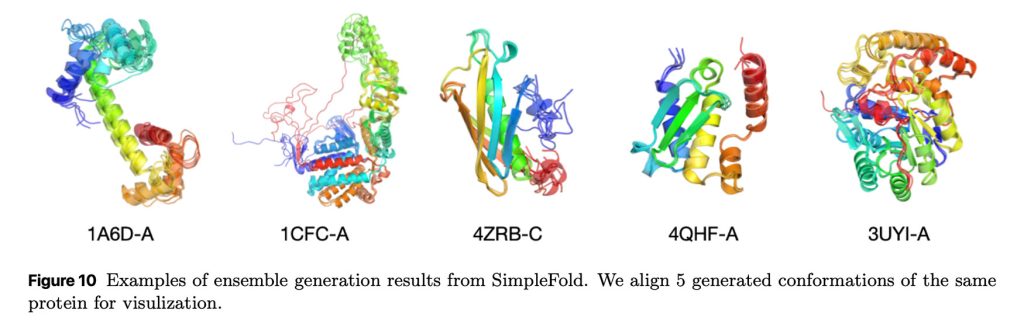
Les chercheurs ont testé SimpleFold à différents niveaux de complexité, allant de 100 millions à 3 milliards de paramètres. Les évaluations réalisées sur des benchmarks reconnus, tels que CAMEO22 et CASP14, ont confirmé des résultats encourageants.
SimpleFold s’est montré compétitif face aux modèles établis, atteignant environ 95 % des performances d’AlphaFold2 dans de nombreux cas, tout en étant moins gourmand en ressources. Notamment, le modèle le plus simple a démontré une efficacité comparable à des modèles plus complexes.
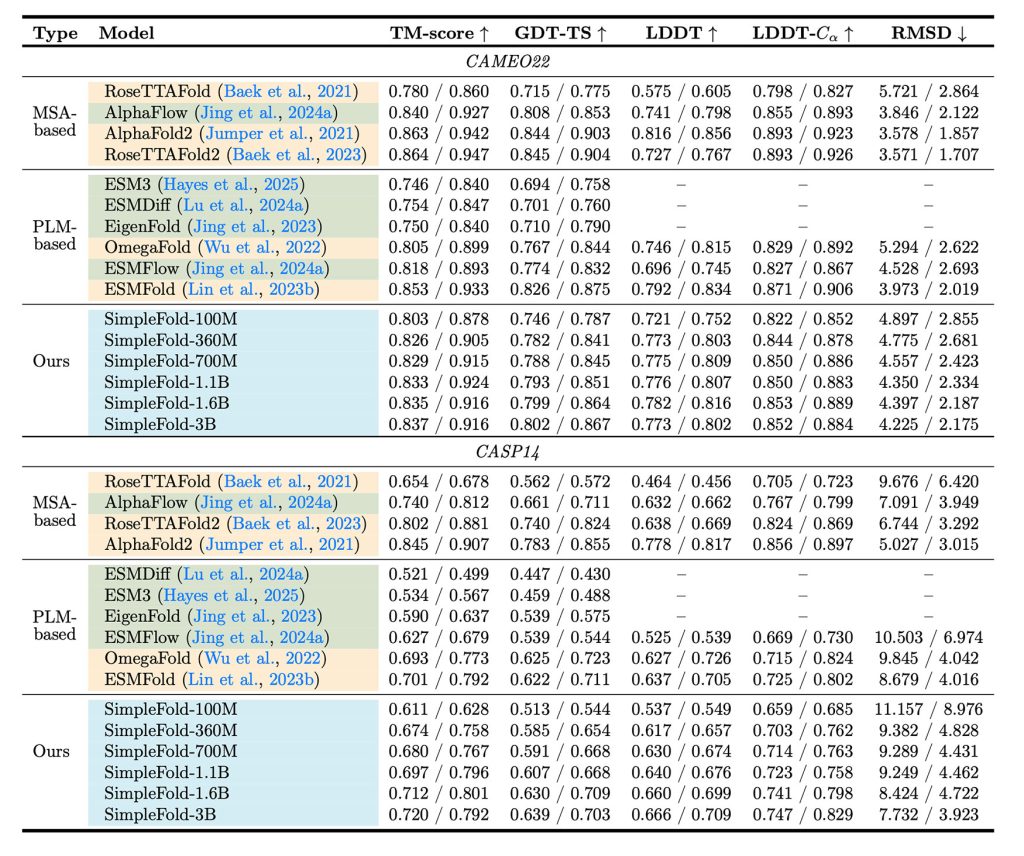
Les résultats ont montré qu’en augmentant la taille des modèles, les performances s’améliorent. Ce constat pourrait être essentiel pour l’avenir des modèles de prédiction protéique, incitant les chercheurs à explorer davantage cette voie.
SimpleFold représente une avancée prometteuse, mais les chercheurs insistent sur le fait qu’il ne s’agit que du commencement. Ils espèrent que cet outil inspirera d’autres chercheurs à développer des modèles génératifs de protéines performants et accessibles.